Cartas al Editor
Utilidad de MALDITOF-MS para identificación de uropatógenos desde muestra directa
Use of MALDITOF-MS for direct identification from urine
Actual. Med. 2015; 100: (795): 103-104 DOI: 10.15568/am.2015.795.cd02
Enviado:02-04-2015
Revisado:30-05-2015
Aceptado:30-06-2015
Leer Artículo Completo
Sr. Editor:
Las Infecciones del Tracto Urinario (ITUs) son una de las causas de infección bacteriana más comunes (1). El cultivo bacteriano sigue siendo el “gold standard” para el diagnóstico de una ITU, sin embargo requiere de 48 a 72 horas para obtener un resultado definitivo. En casos de pacientes graves hospitalizados, acelerar el tiempo hacia el diagnóstico puede tener importantes consecuencias.
La espectrometría de masas MALDI-TOF (Matrix-assisted laser desorption ionization–time of flight) se está convirtiendo en un método fiable para la identificación de microorganismos (2,3). Se han descrito protocolos que permiten la identificación directamente desde la orina mediante MALDITOF-MS (4,5). El objetivo de este trabajo ha sido determinar la utilidad de MALDITOF-MS en la detección de uropatógenos directamente desde la muestra de orina, previa realización de un tratamiento adaptado a nuestro laboratorio.
Entre julio y septiembre de 2014 se seleccionaron en el laboratorio de Microbiología y Parasitología del Hospital Universitario San Cecilio de Granada un total de 300 muestras de orina que resultaron positivas mediante el sistema automatizado Sysmex UF1000i (Roche Diagnostics). Las muestras positivas se cultivaron en medio de McConkey y Agar Sangre (Becton Dickinson) y se incubaron a 37ºC durante 18-24 horas, identificando las colonias mediante MALDITOF-MS en aquellas muestras que se consideraron positivas (>105 UFC/ml). Por otra parte, una alícuota de cada orina se conservó a 4ºC durante 24 horas y posteriormente se centrifugó a 2500 rpm durante 1 minuto, recogiendo el sobrenadante que fue centrifugado a 3700 rpm durante 15 minutos. Este nuevo sobrenadante fue eliminado y el sedimento, tras ser lavado con 1 mL de agua destilada estéril, se centrifugó a 3700 rpm durante 15 minutos. A partir de 1 microlitro de este último sedimento se realizó la identificación mediante MALDITOF-MS.
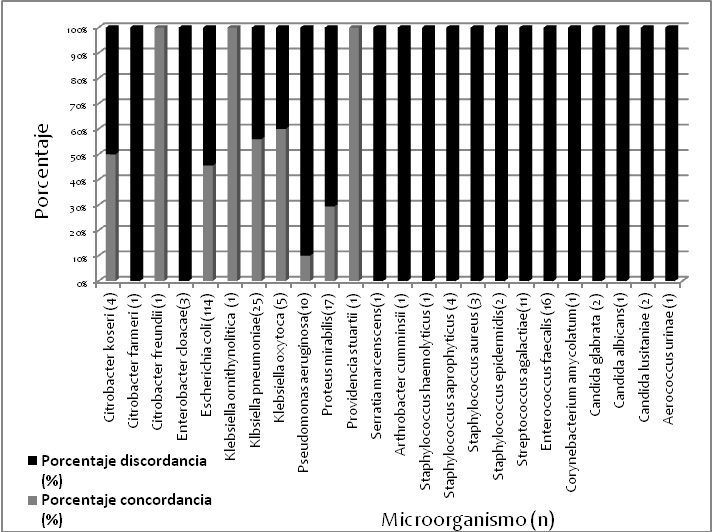
De las 300 muestras analizadas, 230 fueron positivas por cultivo (76,6%) y 70 negativas o contaminadas. MALDITOF no identificó microorganismos en ninguna de las muestras que resultaron negativas o contaminadas mediante cultivo habitual. La identificación con MALDITOF-MS a partir de muestra de orina y de cultivo coincidieron en 80 casos (34,8%). No se obtuvo identificación desde muestra directa de ningún patógeno grampositivo ni levaduras (figura 1). Entre los gramnegativos se obtuvo identificación concordante por ambas técnicas en un 43,7% de los casos (80/183). La sensibilidad de identificación desde muestra directa fue del 34,8%, la especificidad del 100% y los valores predictivos positivo y negativo del 100% y 58,3% respectivamente.
Figura 1. Comparación de los porcentajes de identificación según microorganismo.
Los resultados obtenidos en nuestro estudio presentan menores valores de sensibilidad que los obtenidos en otros similares (4,5). Aunque para microorganismos gramnegativos la sensibilidad del test es mayor (43.7%), y la especificidad es muy alta (100%), pensamos que este tipo de protocolo de identificación rápida no puede ser utilizado en la rutina clínica, ya que sólo en un número limitado de casos aportaría ventajas sobre el cultivo convencional. Aunque este estudio no se ha diseñado como un estudio de coste-eficacia, parece razonable pensar que la sensibilidad no avalaría los costes de material y los recursos humanos empleados en aplicar esta tecnología.
REFERENCIAS
- Foxman B, Barlow R, D’Arcy H, Gillespie B, Sobel JD. Urinary tract infection: self-reported incidence and associated costs. Ann. Epidemiol. 2000;10:509–15.
- Fenselau C, Demirev PA. Characterization of intact microorganisms by MALDI mass spectrometry. Mass Spectrom Rev 2001; 20: 157–171.
- García P, Allende F, Legarraga P, Huilcaman M, Solari S. Bacterial identification based on protein mass spectrometry: A new insight at the microbiology of the 21st century. Rev Chilena Infectol. 2012;29(3):263-72.
- Ferreira L, Sánchez-Juanes F, González-Ávila M, Cembrero-Fuciños D, Herrero-Hernández A, González-Buitrago JM, et al. Direct identification of urinary tract pathogens from urine samples by matrix-assisted laser desorption Ionization-time of flight mass spectrometry. J Clin Microbiol. 2010;48(6):2110.
- Ferreira L, Sánchez-Juanes F, Muñoz-Bellido JL, González-Buitrago JM. Rapid method for direct identification of bacteria in urine and blood culture samples by matrix-assisted laser desorption ionization time-of-flight mass spectrometry: intact cell vs. extraction method. Clin Microbiol Infect. 2011;17: 1007-12.
INFORMACIÓN DEL ARTÍCULO
Autora para la correspondencia: María de la Paz Casas Hidalgo. Avenida de Andalucía nº7,2ºB. 18014 Granada. Tlfno: 958272065 – 654093477 Email: inp880@hotmail.com